Modern views on the role of X gene of the hepatitis B virus (Hepadnaviridae: Orthohepadnavirus: Hepatitis B virus) in the pathogenesis of the infection it causes
- Authors: Panasiuk Y.V.1, Vlasenko N.V.1, Churilova N.S.1, Klushkina V.V.1, Dubodelov D.V.1, Kudryavtseva E.N.1, Korabelnikova M.I.1, Rodionova Z.S.1, Semenenko T.A.2, Kuzin S.N.1, Akimkin V.G.1
-
Affiliations:
- FSBI «Central Research Institute for Epidemiology» of the Federal Service for Supervision of Consumer Rights Protection and Human Wellbeing (Rospotrebnadzor)
- FSBI «National Research Centre for Epidemiology and Microbiology named after the honorary academician N.F. Gamaleya» of the Ministry of Health of Russia
- Issue: Vol 67, No 1 (2022)
- Pages: 7-17
- Section: REVIEWS
- URL: https://ogarev-online.ru/0507-4088/article/view/118180
- DOI: https://doi.org/10.36233/0507-4088-84
- ID: 118180
Cite item
Abstract
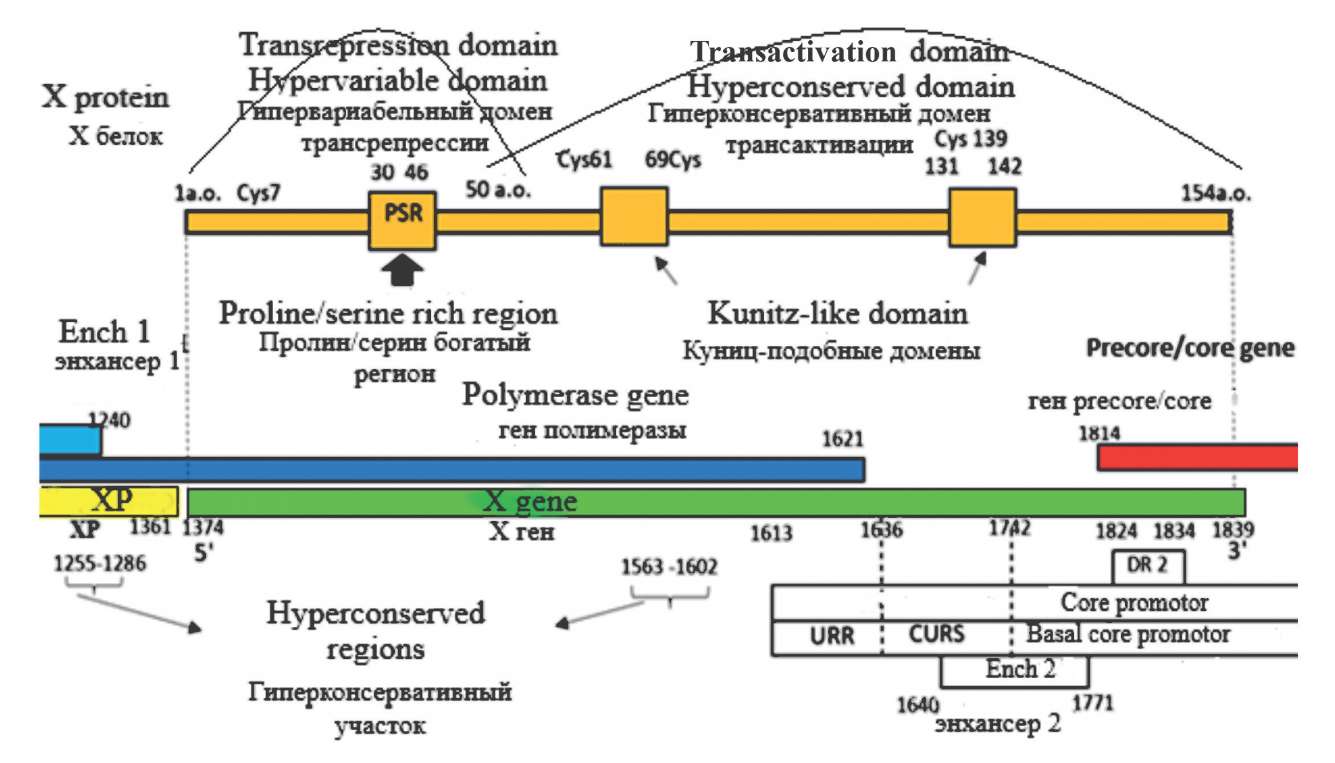
The review presents information on the role of hepatitis B virus (Hepadnaviridae: Orthohepadnavirus: Hepatitis B virus) (HBV) X gene and the protein it encodes (X protein) in the pathogenesis of viral hepatitis B. The evolution of HBV from primordial to the modern version of hepadnaviruses (Hepadnaviridae), is outlined as a process that began about 407 million years ago and continues to the present. The results of scientific works of foreign researchers on the variety of the influence of X protein on the infectious process and its role in the mechanisms of carcinogenesis are summarized. The differences in the effect of the X protein on the course of the disease in patients of different ethnic groups with regard to HBV genotypes are described. The significance of determining the genetic variability of X gene as a fundamental characteristic of the virus that has significance for the assessment of risks of hepatocellular carcinoma (HCC) spread among the population of the Russian Federation is discussed.
Full Text
##article.viewOnOriginalSite##About the authors
Y. V. Panasiuk
FSBI «Central Research Institute for Epidemiology» of the Federal Service for Supervision of Consumer Rights Protection and Human Wellbeing (Rospotrebnadzor)
Author for correspondence.
Email: epidbsmp@mail.ru
ORCID iD: 0000-0002-9335-4953
Panasiuk Ya.V., Physician-Epidemiologist of the Viral Hepatitis Laboratory, Department of Molecular Diagnostics and Epidemiology
Moscow, 111123
Russian FederationN. V. Vlasenko
FSBI «Central Research Institute for Epidemiology» of the Federal Service for Supervision of Consumer Rights Protection and Human Wellbeing (Rospotrebnadzor)
ORCID iD: 0000-0002-2388-1483
Moscow, 111123
Russian FederationN. S. Churilova
FSBI «Central Research Institute for Epidemiology» of the Federal Service for Supervision of Consumer Rights Protection and Human Wellbeing (Rospotrebnadzor)
ORCID iD: 0000-0001-5344-5829
Moscow, 111123
Russian FederationV. V. Klushkina
FSBI «Central Research Institute for Epidemiology» of the Federal Service for Supervision of Consumer Rights Protection and Human Wellbeing (Rospotrebnadzor)
ORCID iD: 0000-0001-8311-8204
Moscow, 111123
Russian FederationD. V. Dubodelov
FSBI «Central Research Institute for Epidemiology» of the Federal Service for Supervision of Consumer Rights Protection and Human Wellbeing (Rospotrebnadzor)
ORCID iD: 0000-0003-3093-5731
Moscow, 111123
Russian FederationE. N. Kudryavtseva
FSBI «Central Research Institute for Epidemiology» of the Federal Service for Supervision of Consumer Rights Protection and Human Wellbeing (Rospotrebnadzor)
ORCID iD: 0000-0002-7325-8577
Moscow, 111123
Russian FederationM. I. Korabelnikova
FSBI «Central Research Institute for Epidemiology» of the Federal Service for Supervision of Consumer Rights Protection and Human Wellbeing (Rospotrebnadzor)
ORCID iD: 0000-0002-2575-8569
Moscow, 111123
Russian FederationZ. S. Rodionova
FSBI «Central Research Institute for Epidemiology» of the Federal Service for Supervision of Consumer Rights Protection and Human Wellbeing (Rospotrebnadzor)
ORCID iD: 0000-0002-2575-8569
Moscow, 111123
Russian FederationT. A. Semenenko
FSBI «National Research Centre for Epidemiology and Microbiology named after the honorary academician N.F. Gamaleya» of the Ministry of Health of Russia
ORCID iD: 0000-0002-6686-9011
123098, Moscow
Russian FederationS. N. Kuzin
FSBI «Central Research Institute for Epidemiology» of the Federal Service for Supervision of Consumer Rights Protection and Human Wellbeing (Rospotrebnadzor)
ORCID iD: 0000-0002-0616-9777
Moscow, 111123
Russian FederationV. G. Akimkin
FSBI «Central Research Institute for Epidemiology» of the Federal Service for Supervision of Consumer Rights Protection and Human Wellbeing (Rospotrebnadzor)
ORCID iD: 0000-0003-4228-9044
Moscow, 111123
Russian FederationReferences
- WHO. Hepatitis B: Fact sheet. Available at: https://www.who.int/newsroom/fact-sheets/detail/hepatitis-b (accessed November 29, 2021).
- Sung H., Ferlay J., Siegel R.L., Laversanne M., Soerjomataram I., Jemal A., et.al. Global Cancer Statistics 2020: GLOBOCAN estimates of incidence and mortality worldwide for 36 cancers in 185 countries. CA Cancer J. Clin. 2020; 71(3): 209–49. https://doi.org/10.3322/caac.21660
- Ющук Н.Д., Климова Е.А., Знойко О.О., Кареткина Г.Н., Максимов С.Л., Маев И.В. Вирусные гепатиты: клиника, диагностика, лечение. М.: ГЭОТАР-Медиа; 2014.
- Revill P.A., Tu T., Netter H.J., Yuen L.K.W., Locarnini S.A., Littlejohn M. The evolution and clinical impact of hepatitis B virus genome diversity. Nat. Rev. Gastroenterol. Hepatol. 2020; 17(10): 618–34. https://doi.org/10.1038/s41575-020-0296-6
- Datta S. An overview of molecular epidemiology of hepatitis B virus (HBV) in India. Virol. J. 2008; 5: 156. https://doi.org/10.1186/1743-422X-5-156
- Tuteja A., Siddiqui A.B., Madan K., Goyal R., Shalimar, Sreenivas V., et al. Mutation profiling of the hepatitis B virus strains circulating in North Indian population. PLoS One. 2014; 9(3): e91150. https://doi.org/10.1371/journal.pone.0091150
- Tarocchi M., Polvani S., Marroncini G., Galli A. Molecular mechanism of hepatitis B virus-induced hepatocarcinogenesis. World J. Gastroenterol. 2014; 20(33): 11630–40. https://doi.org/10.3748/wjg.v20.i33.11630
- Levrero M., Zucman-Rossi J. Mechanisms of HBV-induced hepatocellular carcinoma. J. Hepatol. 2016; 64(1 Suppl.): S84–101. https://doi.org/10.1016/j.jhep.2016.02.021
- Lau K.C.K., Burak K.W., Coffin C.S. Impact of hepatitis B virus genetic variation, integration, and lymphotropism in antiviral treatment and oncogenesis. Microorganisms. 2020; 8(10): 1470. https://doi.org/10.3390/microorganisms8101470
- Godoy C., Tabernero D., Sopena S., Gregori J., Cortese M.F., González C., et al. Characterization of hepatitis B virus X gene quasispecies complexity in mono-infection and hepatitis delta virus superinfection. World J. Gastroenterol. 2019; 25(13): 1566–79. https://doi.org/10.3748/wjg.v25.i13.1566
- Sung W.K., Lu Y., Lee C.W.H., Zhang D., Ronaghi M., Lee C.G.L. Deregulated direct targets of the hepatitis B virus (HBV) protein, HBx, identified through chromatin immunoprecipitation and expression microarray profiling. J. Biol. Chem. 2009; 284(33): 21941–54. https://doi.org/10.1074/jbc.M109.014563
- van Hemert F.J., van de Klundert M.A.A., Lukashov V.V., Kootstra N.A., Berkhout B., Zaaijer H.L., et al. Protein X of hepatitis B virus: origin and structure similarity with the central domain of DNA glycosylase. PLoS One. 2011; 6(8): e23392. https://doi.org/10.1371/journal.pone.0023392
- Al-Qahtani A.A., Al-Anazi M.R., Nazir N., Ghai R., Abdo A.A., Sanai F.M., et al. Hepatitis B virus (HBV) X gene mutations and their association with liver disease progression in HBV-infected patients. Oncotarget. 2017; 8(62): 105115–25. https://doi.org/10.18632/oncotarget.22428
- Rahmani Z., Huh K.W., Lasher R., Siddiqui A. Hepatitis B virus X protein colocalizes to mitochondria with a human voltage-dependent anion channel, HVDAC3, and alters its transmembrane potential. J. Virol. 2000; 74(6): 2840–6. https://doi.org/10.1128/jvi.74.6.2840-2846.2000
- Salpini R., Surdo M., Cortese M.F., Palumbo G.A., Carioti L., Cappiello G., et al The novel HBx mutation F30V correlates with hepatocellular carcinoma in vivo, reduces hepatitis B virus replicative efficiency and enhances anti-apoptotic activity of HBx N terminus in vitro. Clin. Microbiol. Infect. 2019; 25(7): 906.e1–7. https://doi.org/10.1016/j.cmi.2018.11.017
- Chang S.F., Netter H.J., Hildt E., Schuster R., Schaefer S., Hsu Y.C., et al. Duck hepatitis B virus expresses a regulatory HBx-like protein from a hidden open reading frame. J. Virol. 2001; 75(1): 161–70. https://doi.org/10.1128/JVI.75.1.161-170.2001
- Bouchard M.J., Schneider R.J. The enigmatic X gene of hepatitis B virus. J. Virol. 2004; 78(23): 12725–34. https://doi.org/10.1128/JVI.78.23.12725-12734.2004
- Gómez-Gonzalo M., Carretero M., Rullas J., Lara-Pezzi E., Aramburu J., Berkhout B., et al. The hepatitis B virus X protein induces HIV-1 replication and transcription in synergy with T-cell activation signals: functional roles of NF-κB/NF-AT and SP1-binding sites in the HIV-1 long terminal repeat promoter. J. Biol. Chem. 2001; 276(38): 35435–43. https://doi.org/10.1074/jbc.M103020200
- González C., Tabernero D., Cortese M.F., Gregori J., Casillas R., Riveiro-Barciela M., et al. Detection of hyper-conserved regions in hepatitis B virus X gene potentially useful for gene therapy. World J. Gastroenterol. 2018; 24(19): 2095–107. https://doi.org/10.3748/wjg.v24.i19.2095
- Kim H., Lee S.A., Kim B.J. X region mutations of hepatitis B virus related to clinical severity. World J. Gastroenterol. 2016; 22(24): 5467–78. https://doi.org/10.3748/wjg.v22.i24.5467
- Suh A., Brosius J., Schmitz J., Kriegs J.O. The genome of a Mesozoic paleovirus reveals the evolution of hepatitis B viruses. Nat. Commun. 2013; 4: 1791. https://doi.org/10.1038/ncomms2798
- Suh A., Weber C.C., Kehlmaier C., Braun E.L., Green R.E., Fritz U., et al. Early Mesozoic Coexistence of Amniotes and Hepadnaviridae. PLoS Genet. 2014; 10(12): e1004559. https://doi.org/10.1371/journal.pgen.1004559
- Lauber C., Seitz S., Mattei S., Suh A., Beck J., Herstein J., et al. Deciphering the origin and evolution of hepatitis B viruses by means of a family of non-enveloped fish viruses. Cell Host Microbe. 2017; 22(3): 387–99.e6. https://doi.org/10.1016/j.chom.2017.07.0192
- Pesavento P.A., Jackson K., Scase T., Tse T., Hampson B., Munday J.S., et al. A novel hepadnavirus is associated with chronic hepatitis and hepatocellular carcinoma in cats. Viruses. 2019; 11(10): 969. https://doi.org/10.3390/v11100969
- Bonvicino C.R., Moreira M.A., Soares M.A. Hepatitis B virus lineages in mammalian hosts: potential for bidirectional cross-species transmission. World J. Gastroenterol. 2014; 20(24): 7665–74. https://doi.org/10.3748/wjg.v20.i24.7665
- Hu X., Javadian A., Gagneux P., Robertson B.H. Paired chimpanzee hepatitis B virus (ChHBV) and mtDNA sequences suggest different ChHBV genetic variants are found in geographically distinct chimpanzee subspecies. Virus. Res. 2001; 79(1-2): 103–8. https://doi.org/10.1016/s0168-1702(01)00334-3
- He B., Fan Q., Yang F., Hu T., Qiu W., Feng Y., et al. Hepatitis virus in long-fingered bats, Myanmar. Emerg. Infect. Dis. 2013; 19(4): 638–40. https://doi.org/10.3201/eid1904.121655
- Li W., She R., Liu L., You H., Yin J. Prevalence of a virus similar to human hepatitis B virus in swine. Virol. J. 2010; 7: 60. https://doi.org/10.1186/1743-422x-7-60
- Sa-Nguanmoo P., Rianthavorn P., Amornsawadwattana S., Poovorawan Y. Hepatitis B virus infection in non-human primates. Acta Virol. 2009; 53(2): 73–82. https://doi.org/10.4149/av_2009_02_73
- Lanford R.E., Chavez D., Brasky K.M., Burns R.B. III, Rico-Hesse R. Isolation of a hepadnavirus from the woolly monkey, a New World primate. Proc. Natl Acad. Sci. USA. 1998; 95(10): 5757–61. https://doi.org/10.1073/pnas.95.10.5757
- Tian J., Xia K., She R., Li W., Ding Y., Wang J., et al. Detection of Hepatitis B virus in serum and liver of chickens. Virol. J. 2012; 9: 2. https://doi.org/10.1186/1743-422X-9-2
- Summers J., Smolec J.M., Snyder R. A virus similar to human hepatitis B virus associated with hepatitis and hepatoma in woodchucks. Proc. Natl Acad. Sci. USA. 1978; 75(9): 4533–7. https://doi.org/10.1073/pnas.75.9.4533
- Mason W.S., Seal G., Summers J. Virus of Pekin ducks with structural and biological relatedness to human hepatitis B virus. J. Virol. 1980; 36(3): 829–36. https://doi.org/10.1128/JVI.36.3.829-836.1980
- Sprengel R., Kaleta E.F., Will H. Isolation and characterization of a hepatitis B virus endemic in herons. J. Virol. 1988; 62(10): 3832–9. https://doi.org/10.1128/JVI.62.10.3832-3839.1988
- Chang S.F., Netter H.J., Bruns M., Schneider R., Frölich K., Will H. A new avian hepadnavirus infecting snow geese (Anser caerulescens) produces a significant fraction of virions containing single-stranded DNA. Virology. 1999; 262(1): 39–54. https://doi.org/10.1006/viro.1999.9844
- Pult I., Netter H.J., Bruns M., Prassolov A., Sirma H., Hohenberg H., et al. Identification and analysis of a new hepadnavirus in white storks. Virology. 2001; 289(1): 114–28. https://doi.org/10.1006/viro.2001.1115
- Prassolov A., Hohenberg H., Kalinina T., Schneider C., Cova L., Krone O., et al. New hepatitis B virus of cranes that has an unexpected broad host range. J. Virol. 2003; 77(3): 1964–76. https://doi.org/10.1128/jvi.77.3.1964-1976.2003
- Lauber C., Seitz S., Mattei S., Suh A., Beck J., Herstein J., et al. Deciphering the origin and evolution of hepatitis B viruses by means of a family of non-enveloped fish viruses. Cell Host Microbe. 2017; 22(3): 387–99.e6. https://doi.org/10.1016/j.chom.2017.07.0192
- Meier A., Mehrle S., Weiss T.S., Mier W., Urban S. Myristoylated PreS1-domain of the hepatitis B virus L-protein mediates specific binding to differentiated hepatocytes. Hepatology. 2013; 58(1): 31–42. https://doi.org/10.1002/hep.26181
- Kumar V., Jayasuryan N., Kumar R. A truncated mutant (residues 58–140) of the hepatitis B virus X protein retains transactivation function. Proc. Natl Acad. Sci. USA. 1996; 93(11): 5647–52. https://doi.org/10.1073/pnas.93.11.5647
- Qadri I., Maguire H.F., Siddiqui A. Hepatitis B virus transactivator protein X interacts with the TATA-binding protein. Proc. Natl Acad. Sci. USA. 1995; 92(4): 1003–7. https://doi.org/10.1073/pnas.92.4.1003
- Belloni L., Pollicino T., De Nicola F., Guerrieri F., Raffa G., Fanciulli M., et. al. Nuclear HBx binds the HBV minichromosome and modifies the epigenetic regulation of cccDNA function. Proc. Natl Acad. Sci. USA. 2009; 106(47): 19975–9. https://doi.org/10.1073/pnas.0908365106
- Kornyeyev D., Ramakrishnan D., Voitenleitner C., Livingston C.M., Xing W., Hung M., et al. Spatiotemporal analysis of hepatitis B virus X protein in primary human hepatocytes. J. Virol. 2019; 93(16): e00248-19. https://doi.org/10.1128/JVI.00248-19
- Ali A., Abdel-Hafiz H., Suhail M., Al-Mars A., Zakaria M.K., Fatima K., et al. Hepatitis B virus, HBx mutants and their role in hepatocellular carcinoma. World J. Gastroenterol. 2014; 20(30): 10238–48. https://doi.org/10.3748/wjg.v20.i30.10238
- Taylor E.M., Moghraby J.S., Lees J.H., Smit B., Moens P.B., Lehmann A.R. Characterization of a novel human SMC heterodimer homologous to the Schizosaccharomyces pombe Rad18/Spr18 complex. Mol. Biol. Cell. 2001; 12(6): 1583–94. https://doi.org/10.1091/mbc.12.6.1583
- Murphy C.M., Xu Y., Li F., Nio K., Reszka-Blanco N., Li X., et al. Hepatitis B virus X protein promotes degradation of SMC5/6 to enhance HBV replication. Cell Rep. 2016; 16(11): 2846–54. https://doi.org/10.1016/j.celrep.2016.08.026
- Abdul F., Filleton F., Gerossier L., Paturel A., Hall J., Strubin M., et al. Smc5/6 Antagonism by HBx Is an Evolutionarily Conserved Function of Hepatitis B Virus Infection in Mammals. J. Virol. 2018; 92(16): e00769-18. https://doi.org/10.1128/JVI.00769-18
- Rivière L., Gerossier L., Ducroux A., Dion S., Deng Q., Michel M.L., et al. HBx relieves chromatin-mediated transcriptional repression of hepatitis B viral cccDNA involving SETDB1 histone methyltransferase. J. Hepatol. 2015; 63(5): 1093–102. https://doi.org/10.1016/j.jhep.2015.06.023
- Datta S., Banerjee A., Chandra P.K., Biswas A., Panigrahi R., Mahapatra P.K., et al Analysis of hepatitis B virus X gene phylogeny, genetic variability and its impact on pathogenesis: Implications in Eastern Indian HBV carriers. Virology. 2008; 382(2): 190–8. https://doi.org/10.1016/j.virol.2008.09.007
- Su F., Schneider R.J. Hepatitis B virus HBx protein sensitizes cells to apoptotic killing by tumor necrosis factor alpha. Proc. Natl Acad. Sci. USA. 1997; 94(16): 8744–9. https://doi.org/10.1073/pnas.94.16.8744
- Sung W.K. Genome-wide survey of recurrent HBV integration in hepatocellular carcinoma. Nat. Genet. 2012; 44(7): 765–9. https://doi.org/10.1038/ng.2295
- Shafritz D.A., Kew M.C. Identification of integrated hepatitis B virus DNA sequences in human hepatocellular carcinomas. Hepatology. 1981; 1(1): 1–8. https://doi.org/10.1002/hep.1840010102
- Chauhan R., Michalak T.I. Earliest hepatitis B virus-hepatocyte genome integration: sites, mechanism, and significance in carcinogenesis. Hepatoma Res. 2021; 7: 20. http://doi.org/10.20517/2394-5079.2020.136
- Zhang X., You X., Li N., Zhang W., Gagos S., Wang Q. Involvement of hepatitis B virus X gene (HBx) integration in hepatocarcinogenesis via a recombination of HBx/Alu core sequence/subtelomeric DNA. FEBS Lett. 2012; 586(19): 3215–21. https://doi.org/10.1016/j.febslet.2012.06.039
- Wang Y., Wang H., Pan S., Hu T., Shen J., Zheng H., et al. Capable infection of hepatitis B virus in diffuse large B-cell lymphoma. J. Cancer. 2018; 9(9): 1575–81. https://doi.org/10.7150/jca.24384
- Baghbanian M., Hoseini Mousa S.A., Doosti M., Moghimi M. Association between gastric pathology and hepatitis B virus infection in patients with or without Helicobacter pylori. Asian Pac. J. Cancer Prev. 2019; 20(7): 2177–80. https://doi.org/10.31557/APJCP.2019.20.7.2177
- Niedźwiedzka-Rystwej P., Grywalska E., Hrynkiewicz R., Wołącewicz M., Becht R., Roliński J. The double-edged sword role of viruses in gastric cancer. Cancers (Basel). 2020; 12(6): 1680. https://doi.org/10.3390/cancers12061680
- Tagieva N.E., Gizatullin R.Z., Zakharyev V.M., Kisselev L.L. A genome-integrated hepatitis B virus DNA in human neuroblastoma. Gene. 1995; 152(2): 277–8. https://doi.org/10.1016/0378-1119(94)00665-f
- Schulte L.A., López-Gil J.C., Sainz B. Jr., Hermann P.C. The cancer stem cell in hepatocellular carcinoma. Cancers (Basel). 2020; 12(3): 684. https://doi.org/10.3390/cancers12030684
- Sukowati C.H.C., Reyes P.A.C., Tell G., Tiribelli C. Oncogenicity of viral hepatitis B and C in the initiation of hepatic cancer stem cells. Hepatoma Res. 2019; 5: 2. https://doi.org/10.20517/2394-5079.2018.106
- Mani S.K.K., Andrisani O. Hepatitis B virus-associated hepatocellular carcinoma and hepatic cancer stem cells. Genes (Basel). 2018; 9(3): 137. https://doi.org/10.3390/genes9030137
- Suetsugu A., Nagaki M., Aoki H., Motohashi T., Kunisada T., Moriwaki H. Characterization of CD133+ hepatocellular carcinoma cells as cancer stem/progenitor cells. Biochem. Biophys. Res. Commun. 2006; 351(4): 820–4. https://doi.org/10.1016/j.bbrc.2006.10.128
- Li Z. CD133: a stem cell biomarker and beyond. Exp. Hematol. Oncol. 2013; 2(1): 17. https://doi.org/10.1186/2162-3619-2-17
- Hagiwara S., Nishida N., Park A., Komeda Y., Sakurai T., Watanabe T., et al. Contribution of C1485T mutation in the HBx gene to human and murine hepatocarcinogenesis. Sci. Rep. 2017; 7(1): 10440. https://doi.org/10.1038/s41598-017-10570-0
- Hussain Z., Jung H.S., Ryu D.K., Ryu W.S. Genetic dissection of naturally occurring basal core promoter mutations of hepatitis B virus reveals a silent phenotype in the overlapping X gene. J. Gen. Virol. 2009; 90(Pt. 9): 2272–81. https://doi.org/10.1099/vir.0.010421-0
- Sánchez-Tapias J.M., Costa J., Mas A., Bruguera M., Rodés J. Influence of hepatitis B virus genotype on the long-term outcome of chronic hepatitis B in western patients. Gastroenterology. 2002; 123(6): 184–56. https://doi.org/10.1053/gast.2002.37041
- Kim H., Gong J.R., Lee S.A., Kim B.J. Discovery of a novel mutation (X8Del) resulting in an 8-bp deletion in the hepatitis B virus X gene associated with occult infection in Korean vaccinated individuals. PLoS One. 2015; 10(10): e0139551. https://doi.org/10.1371/journal.pone.0139551
- Li W., Goto K., Matsubara Y., Ito S., Muroyama R., Li Q., et al. The characteristic changes in hepatitis B virus X region for hepatocellular carcinoma: a comprehensive analysis based on global data. PLoS One. 2015; 10(5): e0125555. https://doi.org/10.1371/journal.pone.0125555
- Kurbanov F., Tanaka Y., Fujiwara K., Sugauchi F., Mbanya D., Zekeng L., et al. A new subtype (subgenotype) Ac (A3) of hepatitis B virus and recombination between genotypes A and E in Cameroon. J. Gen. Virol. 2005; 86(Pt. 7): 2047–56. https://doi.org/10.1099/vir.0.80922-0
- Wungu C.D.K., Amin M., Ruslan S.E.N., Purwono P.B., Kholili U., Maimunah U., et al. Association between host TNF-α, TGF-β1, p53 polymorphisms, HBV X gene mutation, HBV viral load and the progression of HBV-associated chronic liver disease in Indonesian patients. Biomed. Rep. 2019; 11(4): 145–53. https://doi.org/10.3892/br.2019.1239
- Melegari M., Wolf S.K., Schneider R.J. Hepatitis B virus DNA replication is coordinated by core protein serine phosphorylation and HBx expression. J. Virol. 2005; 79(15): 9810–20. https://doi.org/10.1128/JVI.79.15.9810-9820.2005
- Prieto C., Montecinos J., Jiménez G., Riquelme C., Garrido D., Hernández S., et al. Phosphorylation of phylogenetically conserved amino acid residues confines HBx within different cell compartments of human hepatocarcinoma cells. Molecules. 2021; 26(5): 1254. https://doi.org/10.3390/molecules26051254
- Goto T., Kato N., Ono-Nita S.K., Yoshida H., Otsuka M., Shiratori Y., et al. Large isoform of hepatitis delta antigen activates serum response factor-associated transcription. J. Biol. Chem. 2000; 275(48): 37311-6. https://doi.org/10.1074/jbc.M002947200
Supplementary files