Сравнительное изучение Ухань-подобного и омикрон-подобного вариантов SARS-CoV-2 на экспериментальных животных моделях
- Авторы: Ленева И.А.1, Смирнова Д.И.1, Карташова Н.П.1, Грачева А.В.1, Иванина А.В.1, Глубокова Е.А.1, Корчевая Е.Р.1, Панкратов А.А.2, Трунова Г.В.2, Хохлова В.А.2, Свитич О.А.1, Зверев В.В.1, Файзулоев Е.Б.1
-
Учреждения:
- ФГБНУ «Научно-исследовательский институт вакцин и сывороток имени И.И. Мечникова»
- ФГБУ «Московский научно-исследовательский онкологический институт имени П.А. Герцена» Минздрава России
- Выпуск: Том 67, № 5 (2022)
- Страницы: 439-449
- Раздел: ОРИГИНАЛЬНЫЕ ИССЛЕДОВАНИЯ
- URL: https://ogarev-online.ru/0507-4088/article/view/118243
- DOI: https://doi.org/10.36233/0507-4088-135
- ID: 118243
Цитировать
Полный текст
Аннотация
Введение. Изменчивость SARS-CoV-2 оказалась выше ожидаемой, а появление новых вариантов вызывает обеспокоенность об их потенциально более высокой вирулентности, трансмиссивности, способности уклоняться от иммунных реакций, вызванных предыдущей инфекцией или вакцинацией. В связи с этим важно изучение патогенеза таких вариантов на экспериментальных моделях SARS-CoV-2.
Цель работы – сравнение патогенности вариантов Ухань и BA.1.1 (омикрон) у мышей BALB/c и сирийских хомяков.
Материал и методы. В исследовании использованы штаммы SARS-CoV-2 Dubrovka, филогенетически близкий к штамму Wuhan-Hu-1, и LIA, филогенетически близкий к штамму омикрон, мыши BALB/c, трансгенные мыши B6.Cg-Tg(K18-ACE2)2Prlmn/HEMI Hemizygous for Tg(K18-ACE2)2Prlmn, сирийские золотистые хомяки. Заражение животных проводили интраназально, определение вирулентности выполняли посредством комплекса клинических, патоморфологических и вирусологических методов.
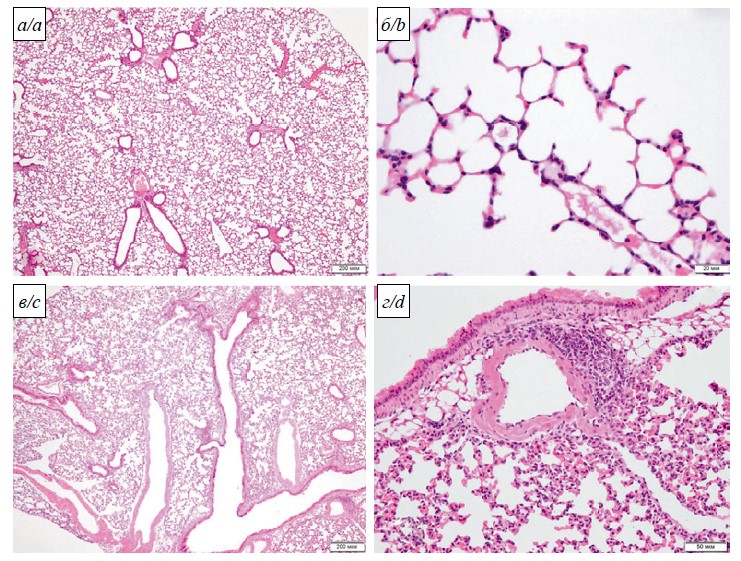
Результаты. Сравнительные исследования штаммов SARS-CoV-2 Dubrovka (Ухань-подобного) и LIA (омикрон-подобного) на моделях животных продемонстрировали их различную патогенность. При параллельном заражении мышей BALB/c вариантами Dubrovka и LIA инфекция протекала без серьёзных клинических признаков и повреждений лёгких. Заражение штаммом LIA приводило к системному заболеванию с высоким содержанием вирусной РНК в лёгких и тканях мозга животных. Вирусная РНК у мышей при заражении штаммом Dubrovka была преходящей и не обнаруживалась в лёгких уже на 7-й день после заражения. Напротив, у хомяков штамм Dubrovka обладал большей патогенностью, чем штамм LIA. При инфицировании штаммом Dubrovka поражения лёгких были значительнее, наблюдались потеря массы тела и распространение вируса по органам, в частности в ткани головного мозга, в то время как при заражении штаммом LIA вирус в тканях головного мозга не определялся.
Заключение. Изучение различных вариантов SARS-CoV-2 у видов, изначально невосприимчивых к инфекции, важно для мониторинга зоонозных резервуаров, создающих риск распространения новых вариантов у людей.
Полный текст
Открыть статью на сайте журналаОб авторах
Ирина Анатольевна Ленева
ФГБНУ «Научно-исследовательский институт вакцин и сывороток имени И.И. Мечникова»
Автор, ответственный за переписку.
Email: wnyfd385@yandex.ru
ORCID iD: 0000-0002-7755-2714
д.б.н., зав. лаб. экспериментальной вирусологии
Россия, 105064, г. МоскваДарья Ильинична Смирнова
ФГБНУ «Научно-исследовательский институт вакцин и сывороток имени И.И. Мечникова»
Email: daria.sm.1995@mail.ru
ORCID iD: 0000-0001-7325-0834
м.н.с., лаб. молекулярной вирусологии
Россия, 105064, г. МоскваНадежда Павловна Карташова
ФГБНУ «Научно-исследовательский институт вакцин и сывороток имени И.И. Мечникова»
Email: nadezdakartasova10571@gmail.com
ORCID iD: 0000-0003-2096-5080
н.с. лаб. экспериментальной вирусологии
Россия, 105064, г. МоскваАнастасия Вячеславовна Грачева
ФГБНУ «Научно-исследовательский институт вакцин и сывороток имени И.И. Мечникова»
Email: anastasiia.gracheva.95@mail.ru
ORCID iD: 0000-0001-8428-4482
м.н.с., лаб. молекулярной вирусологии
Россия, 105064, г. МоскваАнна Валерьевна Иванина
ФГБНУ «Научно-исследовательский институт вакцин и сывороток имени И.И. Мечникова»
Email: ivanina.anna97@mail.ru
ORCID iD: 0000-0002-7289-693X
лаборант-исследователь лаб. экспериментальной вирусологии
Россия, 105064, г. МоскваЕкатерина Андреевна Глубокова
ФГБНУ «Научно-исследовательский институт вакцин и сывороток имени И.И. Мечникова»
Email: eaglubokova@yandex.ru
ORCID iD: 0000-0002-5925-9733
м.н.с., лаб.экспериментальной вирусологии
Россия, 105064, г. МоскваЕкатерина Романовна Корчевая
ФГБНУ «Научно-исследовательский институт вакцин и сывороток имени И.И. Мечникова»
Email: c.korchevaya@gmail.com
ORCID iD: 0000-0002-6417-3301
м.н.с., лаб. молекулярной вирусологии
Россия, 105064, г. МоскваАндрей Александрович Панкратов
ФГБУ «Московский научно-исследовательский онкологический институт имени П.А. Герцена» Минздрава России
Email: andreimnioi@yandex.ru
ORCID iD: 0000-0001-7291-9743
к.б.н., зав. отделением экспериментальной фармакологии и токсикологии
Россия, 125284, г. МоскваГалина В. Трунова
ФГБУ «Московский научно-исследовательский онкологический институт имени П.А. Герцена» Минздрава России
Email: gtrunovamnioi@mail.ru
ORCID iD: 0000-0003-2917-4496
к.б.н., старший научный сотрудник отделения экспериментальной фармакологии и токсикологии
Россия, 125284, г. МоскваВарвара А. Хохлова
ФГБУ «Московский научно-исследовательский онкологический институт имени П.А. Герцена» Минздрава России
Email: nostocus@yandex.ru
ORCID iD: 0000-0002-0339-2068
младший научный сотрудник отделения экспериментальной фармакологии и токсикологии
Россия, 125284, г. МоскваОксана Анатольевна Свитич
ФГБНУ «Научно-исследовательский институт вакцин и сывороток имени И.И. Мечникова»
Email: svitichoa@yandex.ru
ORCID iD: 0000-0003-1757-8389
д.м.н., проф., член-корр. РАН, зав. лаб. молекулярной иммунологии, директор
Россия, 105064, г. МоскваВиталий Васильевич Зверев
ФГБНУ «Научно-исследовательский институт вакцин и сывороток имени И.И. Мечникова»
Email: vitalyzverev@outlook.com
ORCID iD: 0000-0001-5808-2246
д.б.н., проф., академик РАН, зав. лаб. молекулярной биотехнологии
Россия, 105064, г. МоскваЕвгений Бахтиерович Файзулоев
ФГБНУ «Научно-исследовательский институт вакцин и сывороток имени И.И. Мечникова»
Email: faizuloev@mail.ru
ORCID iD: 0000-0001-7385-5083
к.б.н., зав. лаб. молекулярной вирусологии
Россия, 105064, г. МоскваСписок литературы
- Holmes E.C., Goldstein S.A., Rasmussen A.L., Robertson D.L., Crits-Christoph A., Wertheim J.O., et al. The origins of SARS-CoV-2: A critical review. Cell. 2021; 184(19): 4848–56. https://doi.org/10.1016/j.cell.2021.08.017
- Rasmussen A.L. On the origins of SARS-CoV-2. Nat. Med. 2021; 27(1): 9. https://doi.org/10.1038/s41591-020-01205-5
- Trinité B., Pradenas E., Marfil S., Rovirosa C., Urrea V., TarrésFreixas F., et al. Previous SARS-CoV-2 infection increases B.1.1.7 cross-neutralization by vaccinated individuals. Viruses. 2021; 13(6): 1135. https://doi.org/10.3390/v13061135
- Wang P., Nair M.S., Liu L., Iketani S., Luo Y., Guo Y., et al. Antibody resistance of SARS-CoV-2 variants B.1.351 and B.1.1.7. Nature. 2021; 593(7857): 130–5. https://doi.org/10.1038/s41586-021-03398-2
- Mullen J.L., Tsueng G., Latif A.A., Alkuzweny M., Cano M., Haag E., et al. Center for Viral Systems Biology. Outbreak.info. 2020. Available at: https://outbreak.info/
- Wang R., Chen J., Gao K., Hozumi Y., Yin C., Wei G.W. Analysis of SARS-CoV-2 mutations in the United States suggests presence of four substrains and novel variants. Commun. Biol. 2021; 4(1): 228. https://doi.org/10.1038/s42003-021-01754-6
- Dejnirattisai W., Zhou D., Supasa P., Liu C., Mentzer A.J., Ginn H.M., et al. Antibody evasion by the P.1 strain of SARS-CoV-2. Cell. 2021; 184(11): 2939–54.e9. https://doi.org/10.1016/j.cell.2021.03.055
- Planas D., Bruel T., Grzelak L., Guivel-Benhassine F., Staropoli I., Porrot F., et al. Sensitivity of infectious SARS-CoV-2 B.1.1.7 and B.1.351 variants to neutralizing antibodies. Nat. Med. 2021; 27(5): 917–24. https://doi.org/10.1038/s41591-021-01318-5
- Dhar M.S., Marwal R., Vs R., Ponnusamy K., Jolly B., Bhoyar R.C., et al. Genomic characterization and epidemiology of an emerging SARS-CoV-2 variant in Delhi, India. Science. 2021; 374(6570): 995–9. https://doi.org/10.1126/science.abj9932
- Parums D. Editorial: Revised World Health Organization (WHO) terminology for variants of concern and variants of interest of SARS-CoV-2. Med. Sci. Monit. 2021; 27: e933622. https://doi.org/10.12659/MSM.933622
- Karim S.S.A., Karim Q.A. Omicron SARS-CoV-2 variant: a new chapter in the COVID-19 pandemic. Lancet. 2021; 398(10317): 2126–8. https://doi.org/10.1016/S0140-6736(21)02758-6
- Allen H., Tessier E., Turner C., Anderson C., Blomquist P., Simons D., et al. Comparative transmission of SARS-CoV-2 Omicron (B.1.1.529) and Delta (B.1.617.2) variants and the impact of vaccination: national cohort study, England. medRxiv. 2022. Preprint. https://doi.org/10.1101/2022.02.15.22271001
- Lambrou A.S., Shirk P., Steele M.K., Paul P., Paden C.R., Cadwell B., et al. Genomic surveillance for SARS-CoV-2 variants: Predominance of the Delta (B.1.617.2) and omicron (B.1.1.529) variants – United States, June 2021 – January 2022. MMWR Morb. Mortal. Wkly Rep. 2022; 71(6): 206–11. https://doi.org/10.15585/mmwr.mm7106a4
- Petersen E., Ntoumi F., Hui D.S., Abubakar A., Kramer L.D., Obiero C., et al. Emergence of new SARS-CoV-2 Variant of Concern Omicron (B.1.1.529) – highlights Africa’s research capabilities, but exposes major knowledge gaps, inequities of vaccine distribution, inadequacies in global COVID-19 response and control efforts. Int. J. Infect. Dis. 2022; 114: 268–72. https://doi.org/10.1016/j.ijid.2021.11.040
- Andrews N., Stowe J., Kirsebom F., Toffa S., Rickeard T., Gallagher E., et al. Covid-19 vaccine effectiveness against the omicron (B.1.1.529) variant. N. Engl. J. Med. 2022; 386(16): 1532–46. https://doi.org/10.1056/NEJMoa2119451
- Grabowski F., Kochańczyk M., Lipniacki T. The spread of SARS-CoV-2 variant omicron with a doubling time of 2.0-3.3 days can be explained by immune evasion. Viruses. 2022; 14(2): 294. https://doi.org/10.3390/v14020294
- Liu L., Iketani S., Guo Y., Chan J.F.W., Wang M., Liu L., et al. Striking antibody evasion manifested by the Omicron variant of SARS-CoV-2. Nature. 2022; 602(7898): 676–81. https://doi.org/10.1038/s41586-021-04388-0
- Planas D., Saunders N., Maes P., Guivel-Benhassine F., Planchais C., Buchrieser J., et al. Considerable escape of SARS-CoV-2 Omicron to antibody neutralization. Nature. 2022; 602(7898): 671–5. https://doi.org/10.1038/s41586-021-04389-z
- Conceicao C., Thakur N., Human S., Kelly J.T., Logan L., Bialy D., et al. The SARS-CoV-2 Spike protein has a broad tropism for mammalian ACE2 proteins. PLoS Biol. 2020; 18(12): e3001016. https://doi.org/10.1371/journal.pbio.3001016
- Liu Y., Hu G., Wang Y., Ren W., Zhao X., Ji F., et al. Functional and genetic analysis of viral receptor ACE2 orthologs reveals a broad potential host range of SARS-CoV-2. Proc. Natl Acad. Sci. USA. 2021; 118(12): e2025373118. https://doi.org/10.1073/pnas.2025373118
- Gretebeck L.M., Subbarao K. Animal models for SARS and MERS coronaviruses. Curr. Opin. Virol. 2015; 13: 123–9. https://doi.org/10.1016/j.coviro.2015.06.009
- Garry R.F. Mutations arising in SARS-CoV-2 spike on sustained human-to-human transmission and human-to-animal passage. Virological. 2021. Available at: https://virological.org/t/mutations-arising-in-sars-cov-2-spike-on-sustained-human-to-human-transmission-and-human-to-animal-passage/578/14
- Bao L., Deng W., Huang B., Gao H., Liu J., Ren L., et al. The pathogenicity of SARS-CoV-2 in hACE2 transgenic mice. Nature. 2020; 583(7818): 830–3. https://doi.org/10.1038/s41586-020-2312-y
- Kant R., Kareinen L., Smura T., Freitag T.L., Jha S.K., Alitalo K., et al. Common laboratory mice are susceptible to infection with the SARS-CoV-2 beta variant. Viruses. 2021; 13(11): 2263. https://doi.org/10.3390/v13112263
- Montagutelli X., Prot M., Levillayer L., Salazar E.B., Jouvion G., Conquet L., et al. bioRxiv. 2021. Preprint. https://doi.org/10.1101/2021.03.18.436013
- Shuai H., Chan J.F.W., Yuen T.T.T., Yoon C., Hu J.C., Wen L., et al. Emerging SARS-CoV-2 variants expand species tropism to murines. EBioMedicine. 2021; 73: 103643. https://doi.org/10.1016/j.ebiom.2021.103643
- Zhang Y.N., Zhang Z.R., Zhang H.Q., Li N., Zhang Q.Y., Li X.D., et al. Different pathogenesis of SARS-CoV-2 Omicron variant in wild-type laboratory mice and hamsters. Signal Transduct. Target. Ther. 2022 Feb 25; 7(1): 62. https://doi.org/10.1038/s41392-022-00930-2
- Imai M., Iwatsuki-Horimoto K., Hatta M., Loeber S., Halfmann PJ., Nakajima N., et al. Syrian hamsters as a small animal model for SARS-CoV-2 infection and countermeasure development. Proc. Natl Acad. Sci USA. 2020; 117(28): 16587–95. https://doi.org/10.1073/pnas.2009799117
- Грачёва А.В., Корчевая Е.Р., Кудряшова А.М., Борисова О.В., Петруша О.А., Смирнова Д.И. и др. Адаптация МТТ-теста для определения нейтрализующих антител к вирусу SARS-CoV-2. Журнал микробиологии, эпидемиологии и иммунобиологии. 2021; 98(3): 253–65. https://doi.org/10.36233/0372-9311-136
- Ramakrishnan M.A. Determination of 50% endpoint titer using a simple formula. World J. Virol. 2016; 5(2): 85–6. https://doi.org/10.5501/wjv.v5.i2.85
- Gracheva A.V., Korchevaya E.R., Ammour Y.I., Smirnova D.I., Sokolova O.S., Glukhov G.S., et al. Immunogenic properties of SARS-CoV-2 inactivated by ultraviolet light. Arch. Virol. 2022; 167(11): 2181–91. https://doi.org/10.1007/s00705-022-05530-7
- Meng B., Abdullahi A., Ferreira I.A.T.M., Goonawardane N., Saito A., Kimura I., et al. Altered TMPRSS2 usage by SARS-CoV-2 Omicron impacts infectivity and fusogenicity. Nature. 2022; 603(7902): 706–14. https://doi.org/10.1038/s41586-022-04474-x
- Suzuki R., Yamasoba D., Kimura I., Wang L., Kishimoto M., Ito J., et al. Attenuated fusogenicity and pathogenicity of SARS-CoV-2 Omicron variant. Nature. 2022; 603(7902): 700–5. https://doi.org/10.1038/s41586-022-04462-1
- Kim Y.I., Kim S.G., Kim S.M., Kim E.H., Park S.J., Yu K.M., et al. Infection and rapid transmission of SARS-CoV-2 in ferrets. Cell Host Microbe. 2020; 27(5): 704–9.e2. https://doi.org/10.1016/j.chom.2020.03.023
Дополнительные файлы